近日,中科院合肥物质院健康所基因组学团队张帆研究员研发了名为CRISPRimmunity的分析服务平台,它是一个识别CRISPR相关重要分子事件及用于基因编辑调节器的交互式网络服务器。该研究成果发表在国际著名期刊Nucleic Acids Research上。
CRISPRimmunity是一个全新的、用户界面友好的网络服务器,旨在提供面向CRISPR的一站式综合分析服务平台,全面注释CRISPR-Cas系统与Anit-CRISPR系统共进化过程中关键分子事件,准确预测Anti-CRISPR蛋白,从头识别新型II类CRISPR-Cas基因座,基于CRISPR阵列信息预测细菌与可移动元件(噬菌体、质粒)之间的相互作用,从更加综合地进化视角理解CRISPR-Cas系统和anti-CRISPR系统。
CRISPR-Cas系统是自然界中原核生物长期演化过程中所形成适应性免疫系统,该系统通过RNA介导的DNA降解抵御外源基因入侵,能够实现高度灵活的特异性靶向,成为现有基因编辑和基因修饰中效率最高、最简便、成本最低的技术之一。新型CRISPR-Cas相关蛋白及Anti-CRISPR蛋白的发现,将进一步加深我们对CRISPR-Cas系统在原核生物中的作用理解,扩展在其他细胞和生物体中进行基因组编辑应用的工具盒。但目前可用的CRISPR-Cas相关数据资源仅仅关注CRISPR-Cas系统或anti-CRISPR系统中的特定领域,忽视两者之间的共同进化关系,因此提供的信息与服务有限,并且缺乏识别新型II类CRISPR-Cas系统的可用方法。
因此,课题组研发了面向CRISPR-Cas系统与Anti-CRISPR系统的综合分析预测平台——CRISPRimmunity。该平台构建了一系列面向CRISPR相关信息的自定义数据库,注释已知的Anti-CRISPR蛋白和Anti-CRISPR相关蛋白、II类CRISPR-Cas系统、CRISPR阵列类型、HTH结构域和可移动遗传元件,以剖析CRISPR-Cas系统与anti-CRISPR系统共进化中关键分子事件;综合了同源分析、关联分析及原噬菌体区域中自靶向事件等多种策略预测Anti-CRISPR蛋白以提高预测的准确性,在99个经实验验证的Acrs和676个非Acrs的数据上对CRISPRimmunity进行测试,Anti-CRISPR蛋白预测准确率达到0.997;首次提供了II类CRISPR-Cas基因座的从头预测算法,鉴定了4个具有不同PAM结构域的Cas9,1个更小的Cpf1,61个C2c10及3个未分类的全新的V型Cas蛋白,其中一部分CRISPR-Cas基因座已经在体外经实验验证了活性。
CRISPRimmunity网络服务器精心设计了图形用户界面,提供多种可视化、自定义设置选项和可导出机器可读格式的详细结果、详细教程,以便不同需求的用户使用;同时提供了在NCBI数据库中18,408株完全测序的细菌及235株含Acr的细菌及208,209株人类肠道微生物中预注释的CRISPR相关重要分子事件的浏览及下载,为未来的实验设计和进一步的数据分析提供参考。此外,CRISPRimmunity提供了本地化版本为计算生物学家批量数据挖掘提供便利。
该研究工作受到国家自然科学基金委、黑龙江省头雁团队原创探索基金、腾讯科学基金、新基石研究员基金和哈工大青年科学家工作室等基金的资助。
文章链接: https://academic.oup.com/nar/advance-article/doi/10.1093/nar/gkad425/7175359
CRISPRimmunity平台链接:http://www.microbiome-bigdata.com/CRISPRimmunity/index/
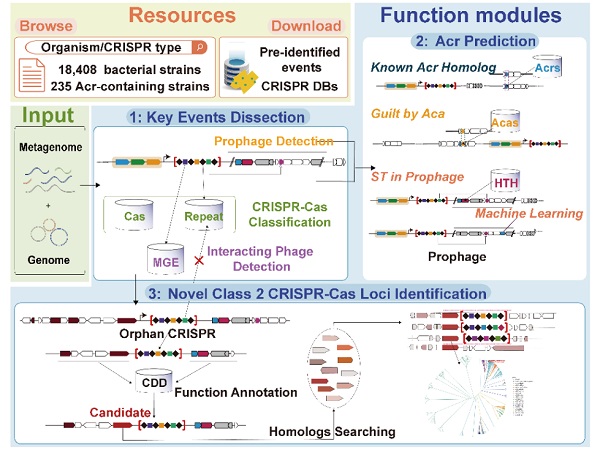
CRISPRimmunity预测分析框架
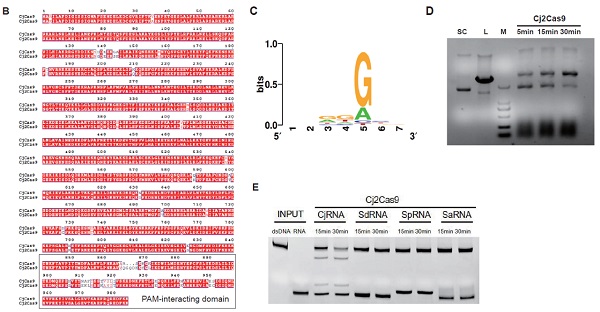
预测的Cj2Cas9所识别的PAM序列的高通量测序分析

CRISPRimmunity结果可视化
